細胞画像のわずかな特徴の違いの見分け方を教えてくれるAIの開発に成功
Press release
Robust Classification of Cell Cycle Phase and Biological Feature Extraction by Image-Based Deep Learning
Yukiko Nagao, Mika Sakamoto, Takumi Chinen, Yasushi Okada, Daisuke Takao Molecular Biology of the Cell 22 Apr 2020 DOI:10.1091/mbc.e20-03-0187東京大学大学院医学系研究科の高尾大輔 助教と東京大学薬学部の長尾幸子 学部生(研究当時)の研究チームは、国立遺伝学研究所の坂本美佳 特任研究員、東京大学大学院薬学系研究科の知念拓実 助教、東京大学国際高等研究所ニューロインテリジェンス国際研究機構(WPI-IRCN)の岡田康志 主任研究者(東京大学大学院医学系研究科・大学院理学系研究科 教授、理化学研究所生命機能科学研究センター(BDR)チームリーダー)らと共同で、ディープラーニングと定量解析により細胞画像から未知の情報を抽出する技術の開発に成功しました。大量の細胞画像から一つ一つの細胞を自動的に切り出し、ディープラーニングにより細胞周期などを判定するAIツールと、その情報をさらに解析することで、細胞周期によって変動する核の形状やゴルジ体の配置パターンなどを抽出する技術を確立しました。これは、人間の目ではとらえにくいわずかな細胞内の変動をAIが発見し、研究者に教えてくれる技術です。
細胞周期によって細胞内の組成や構造は大きく変わることが予想されますが、実際に何がどのように変動するのかを顕微鏡画像から網羅的かつ定量的に解析するためのアプローチは限られていました。具体的に細胞内の何に着目すればいいのかを知るために、今回、共同研究チームはディープラーニングを使って、細胞周期によって変動するパラメータを画像の中から見つける技術を開発しました。これまで研究者が「なんとなく」「経験的に」とらえていた現象や、そもそも見過ごされていた情報を、AIの手助けにより発掘・定量化しようという試みです。その結果、本研究で開発したAIは、DNAやゴルジ体の染色画像の中から、細胞周期によってわずかに変動する特徴を発見しました。この情報を使って共同研究チームが画像を詳しく解析したところ、核やゴルジ体の面積などの特定のパラメータを測定することで画像から細胞周期を分類できることが分かりました。すなわち「画像のどこに着目すれば目的の情報が得られるのかAIが教えてくれる」という研究サポートツールの開発に成功しました。
本研究で開発したツールは汎用性が高く、他の多くの研究への応用を想定しています。細胞周期以外の判定はもちろん、細胞画像以外の画像データへの応用も可能なため、細胞・発生生物学から医療画像の解析など、基礎から応用まで幅広い分野の研究をサポートする強力なツールとなることが期待されます。
本研究は、科学技術振興機構(JST)戦略的創造研究推進事業 チーム型研究(CREST)「統合1細胞解析のための革新的技術基盤」(研究総括:菅野 純夫 東京医科歯科大学 非常勤講師)における「超解像3次元ライブイメージングによるゲノムDNAの構造、エピゲノム状態、転写因子動態の経時的計測と操作」(研究代表者:岡田 康志)および文部科学省世界トップレベル研究拠点プログラム 東京大学国際高等研究所ニューロインテリジェンス国際研究機構(WPI-IRCN)の支援のもとで行われたものです。
また、本研究の一部は以下の事業による支援を受けて行われました。 ・文部科学省 科学研究費 新学術領域研究「学術研究支援基盤形成」先端バイオイメージング支援プラットフォーム(ABiS) ・文部科学省 科学研究費 新学術領域研究「情報物理学でひもとく生命の秩序と設計原理」 ・日本学術振興会科学研究費基盤研究(C)「分子ダイナミクスの定量・操作と数理モデリングによる中心体複製メカニズムの理解」 ・武田科学振興財団 ・島津科学振興財団 ・コニカミノルタ科学技術振興財団
本研究の成果は、2020年4月22日に米国細胞生物学会誌 Molecular Biology of the Cell に掲載されました。
遺伝研の貢献
AI(人工知能)技術を含む細胞画像解析のための情報と技術サポートを提供しました。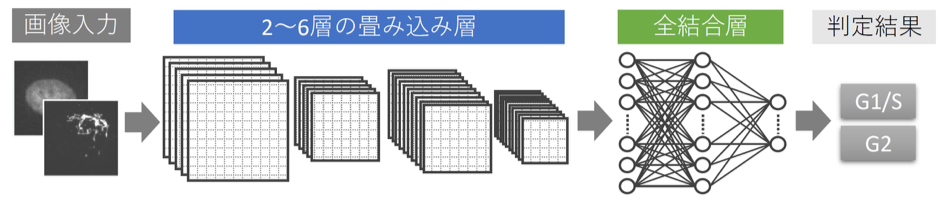
図: AIモデルの模式図 畳み込みニューラルネットワークを使ったディープラーニングモデルを開発した。















