ウェット&ドライによる機能するカイコガエノラーゼ遺伝子群の同定
DBCLS
比較ゲノム解析研究室
先端ゲノミクス推進センター
Identification of functional enolase genes of the silkworm Bombyx mori from public databases with a combination of dry and wet bench processes
Akira Kikuchi, Takeru Nakazato, Katsuhiko Ito, Yosui Nojima, Takeshi Yokoyama, Kikuo Iwabuchi, Hidemasa Bono, Atsushi Toyoda, Asao Fujiyama, Ryoichi Sato and Hiroko Tabunoki
BMC Genomics, 18:83, 2017 DOI:10.1186/s12864-016-3455-y
現在、ネットでゲノム配列情報を簡単に取得できますが、それらの中には間違ったアノテーションが含まれており、その後の機能解析において正確な解釈の妨げになっています。そこで、東京農工大学農学部 天竺桂弘子講師を中心とするグループは、ドライとウェットベンチの連携手法を開発し、公共データベースから生体内で機能しているカイコガ(Bombyx mori)のエノラーゼ遺伝子群を同定しました。
遺伝学研究所 比較ゲノム解析研究室 豊田敦特任教授、同研究所先端ゲノミクス推進センター 藤山秋佐夫特任教授はトランスクリプトーム配列解読をおこない、ライフサイエンス統合データベースセンター(DBCLS) 仲里猛留特任助教、坊農秀雅特任准教授は公共データベース中からの候補遺伝子探索の技術開発をおこなうことで本研究に貢献しました。
またDBCLSが提供する画像・イラスト集Togo Picture Galleryの生物種のイラストが複数のFigure(fig1, fig3)に利用されております。
本研究は、国立遺伝学研究所が有する遺伝研スーパーコンピュータシステムを利用し、また国立遺伝学研究所公募型共同研究 NIG-JOINT (2014-A171 & 2015-A155)の支援を受けました。
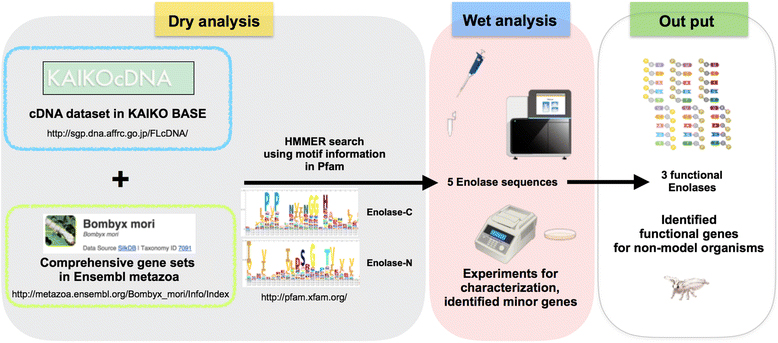
ドライとウェットベンチの連携手法を開発、公共データベースから生体内で機能しているカイコガ(Bombyx mori)のエノラーゼ遺伝子群を同定しました。















