PZLAST-MAG: full length protein sequence similarity search server of large-scale MAG proteins
Koichi Higashi, Hitoshi Ishikawa, Ken Kurokawa, Hiroshi Mori
Bioinformatics Advances(2026)DOI:10.1093/bioadv/vbag129
森宙史准教授と黒川顕教授、データサイエンス共同利用基盤施設バイオ生成AI研究開発センターの東光一准教授とPEZY Computing株式会社の研究グループは、培養困難な環境微生物のゲノムデータとして近年注目されているメタゲノム由来ゲノム(MAG)から得られたタンパク質配列を、超高速で類似性検索できるウェブサーバー「PZLAST-MAG」を開発し、公開しました。PZLAST-MAGは、森グループが中心となって開発し公開しているMAGのデータベースMicrobiome Datahubに収録された21万件以上のMAG由来の約4億配列(1,000億アミノ酸)を検索対象とし、MIMD型メニーコアプロセッサPEZY-SC3上に実装することで、DIAMONDやMMseqs2といった既存ツールに匹敵する精度を保ちながら、5〜15分程度で大規模検索を完了します。
本サーバーの特長は、単なる類似配列の表形式出力にとどまらず、ヒットしたタンパク質の系統的分布、環境オントロジーMEOに基づく生息環境の分布、ゲノムにおける複数クエリの共起パターンを可視化する点にあります(図1)。これにより、機能的に重要な遺伝子のホモログを多様な微生物系統から探索すると同時に、その分類学的・生態学的背景を把握することが可能になります。PZLAST-MAGは登録不要で利用でき、URL(https://pzlast.nig.ac.jp/pzlast/mag)から無料でアクセスできます。本研究開発は、科学技術振興機構(JST)ライフサイエンスデータベース統合事業(統合化推進プログラム)(課題番号:JPMJND2206)、国立研究開発法人新エネルギー・産業技術総合開発機構(NEDO)のグリーンイノベーション基金事業(JPNP22010)、および日本学術振興会 科学研究費助成事業(JSPS KAKENHI)JP22H04925(PAGS)の支援を受けて行われました。
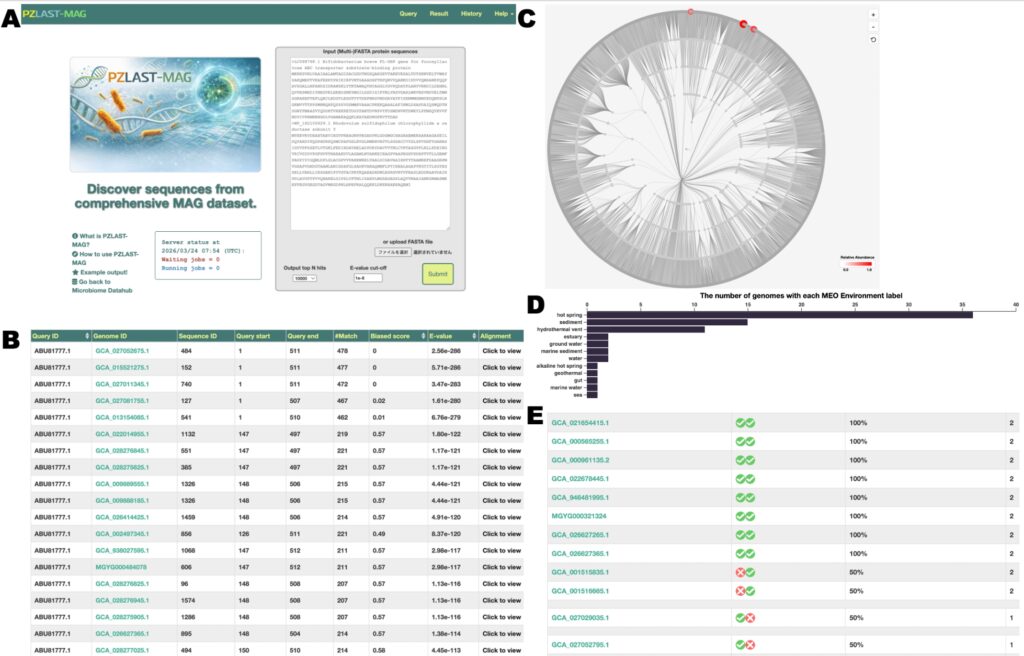
PZLAST-MAG webサーバーの概要。A: 検索画面。B: 表形式の結果表示。C: 系統分岐図上での結果表示。D: ヒットしたMAGの環境分布。E: 複数クエリ配列の場合のMAGごとの共起関係の表示。
