Microbiome Datahub: an open-access platform integrating environmental metadata, taxonomy, and functional annotation forcomprehensive metagenome-assembled genome datasets
Hiroshi Mori, Takatomo Fujisawa, Koichi Higashi, Yasuhiro Tanizawa, Zenichi Nakagawa, Hiroyo Nishide, Masaki Fujiyoshi, Yasukazu Nakamura, Ikuo Uchiyama, Motomu Matsui, Takuji Yamada
Microbiome (2026) DOI: 10.1186/s40168-026-02385-x
環境中の微生物群集から丸ごとDNA配列を解読するメタゲノム解析技術の発展により、培養困難な微生物のメタゲノム由来ゲノム情報(MAG:Metagenome-Assembled Genomes)が爆発的に増加しています。これらのデータは公共の塩基配列リポジトリ(INSD)に登録されていますが、「品質のばらつき」「環境メタデータ(生息場所)の未整理」「遺伝子情報の欠如や分類体系の不統一」といった課題があり、そのままではデータの検索や横断的な比較解析が困難でした。また、既存のMAGの二次データベース(MGnify、IMG/M、SPIRE等)は、登録されたリード配列から独自のパイプラインで「再アセンブリ(再構築)」を行っているため、原著論文で報告されたMAGとは配列が変わってしまい、原著論文の研究成果を正しく参照・評価できないという問題(再現性の喪失)がありました。
森宙史准教授、自然科学研究機構 基礎生物学研究所の内山郁夫准教授、東京科学大学 生命理工学院 山田拓司教授、京都大学 化学研究所 松井求助教を中心とする共同研究グループ(国立遺伝学研究所、基礎生物学研究所、東京科学大学、京都大学、東京大学)は、環境中の微生物を解析したメタゲノム由来のゲノム配列(MAG)を公共の塩基配列リポジトリから網羅的に収集し、環境や系統・遺伝子機能等、様々な情報を付加した統合データベース「MicrobiomeDatahub」を開発・公開しました。本データベースは、公共の塩基配列リポジトリに蓄積された21万件以上のMAG配列に対し、統一された遺伝子予測、系統分類、遺伝子機能アノテーション、表現型予測および環境メタデータを付与したものであり、データ駆動型の微生物学や未知の有用タンパク質探索の基盤として貢献することが期待されます。
Microbiome Datahubは、ウェブ上での高速検索やAPIアクセス、一括ダウンロードに対応しており、基礎的な微生物学研究から、タンパク質構造予測や有用酵素の探索等の応用研究まで、幅広く利用されることが期待されます。本プロジェクトは、今後も急増が予想される公共MAGデータを収載し整理・公開するデータベースとして、継続的な更新と拡張を予定しています。
本研究成果は、科学誌「Microbiome」に2026年3月16日に速報版が掲載されました。
本研究開発は、科学技術振興機構(JST)ライフサイエンスデータベース統合事業(統合化推進プログラム)(課題番号:JPMJND2206)の支援を受けて実施されました。
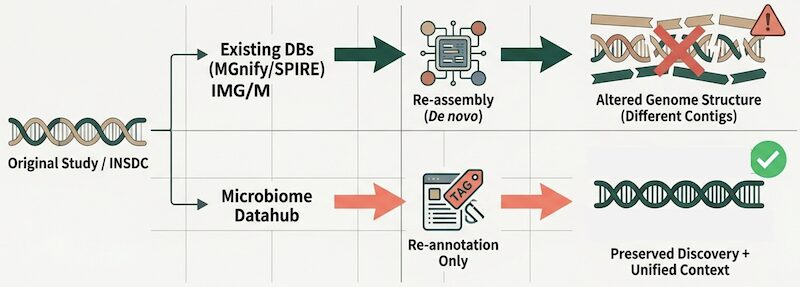
Microbiome Datahubと他の大規模MAGデータベースにおけるMAGの違い
