A curated resource of chemolithoautotrophic genomes and marker genes for CO2 fixation pathway prediction
Shuichi Kawashima, Yoko Okabeppu, Seiha Miyazawa, Natsuko Ichikawa, Hikaru Nagazumi, Yutaka Nishihara, Takeru Nakazato, Susumu Goto, Ken Kurokawa, Masaharu Ishii, Hiroshi Mori
Scientific Data (2025)
微生物によるCO2固定は、炭素が制限された環境で微生物が生息するために不可欠なプロセスであり、地球全体の炭素循環において重要な役割を果たしています。化学合成独立栄養細菌が持つCO2固定経路は多様で、カルビン・ベンソン回路(CBB回路)をはじめとする7種類が知られています。
しかし、これらの経路に関わる酵素遺伝子は多様な系統が所持しており、一部の酵素は複数の経路に関わっているため、ゲノム情報だけでどの経路を持っているかを正確に推定することは困難でした。細菌用の既存の代謝経路予測ツール(METABOLICやgapseqなど)は一般的な代謝経路の予測には有用ですが、多様なCO2固定経路、特に比較的最近発見されたいくつかの経路の予測では、精度に課題がありました。
ゲノム多様性研究室の森宙史准教授と情報・システム研究機データサイエンス共同利用基盤施設 ライフサイエンス統合データベースセンター(DBCLS)、独立行政法人 製品評価技術基盤機構(NITE)、株式会社OKBPなどの共同研究グループは、ゲノム情報から化学合成独立栄養細菌が持つ二酸化炭素(CO2)固定経路を、高精度に予測するソフトウェア「AutoFixMark(オートフィックスマーク)」の開発に成功しました。「AutoFixMark」は、ゲノム配列さえあればCO2固定経路の有無を予測できるため、培養が困難な微生物を含むメタゲノム解析データやシングルセルゲノムへの適用が容易です。本ツールは、環境中における独立栄養細菌の系統的な多様性の解明に役立つだけでなく、CO2を原料として有用物質を生産する微生物の探索など、脱炭素社会の実現に向けたバイオテクノロジーの応用への基盤となることが期待されます。
また、本ツールの開発にあたり、既知の7つのCO2固定経路すべてについて特徴的なマーカー遺伝子を定義しました。さらに、347株の化学合成独立栄養細菌のゲノム情報と保有するCO2固定経路の情報を整備した高品質な参照データセットを構築しました。本研究成果により、メタゲノムやシングルセルゲノム解析などで得られる膨大な微生物ゲノムデータから、CO2を資源として利用できる微生物を効率的に探索することが可能となり、地球規模の炭素循環の理解や、バイオテクノロジーを活用した持続可能なものづくりへの貢献が期待されます。
本研究は主に、国立研究開発法人新エネルギー・産業技術総合開発機構(NEDO)のグリーンイノベーション基金事業(JPNP22010)、および国立研究開発法人科学技術振興機構(JST)NBDC事業推進室の統合化推進プログラム(JPMJND2206)の支援を受けて行われました。
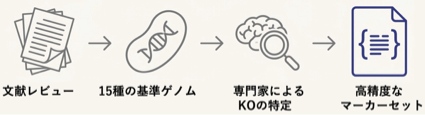
AutoFixMarkにおけるCO2固定経路のマーカー酵素の定義方法
